Descargo de responsabilidad: actualmente, se están realizando importantes actualizaciones al sitio en español sobre COVID-19 que podrían generar demoras en la traducción del contenido. Le pedimos disculpas por los inconvenientes.
Recomendaciones para las personas completamente vacunadas
Página principal del COVID-19
El rol de los CDC en el seguimiento de las variantes
¿Qué están haciendo los CDC para hacer un seguimiento de las variantes del SARS-CoV-2?
En los Estados Unidos, los CDC utilizan la vigilancia genómica para hacer un seguimiento de las variantes emergentes del SARS-CoV-2 que causan el COVID-19. Los CDC establecieron varias vías para conectar los datos de secuencia genómica de los CDC, de laboratorios de salud pública y de laboratorios de diagnóstico comerciales dentro de las bases de datos de acceso público gestionadas por el Centro Nacional de Información Biotecnológica (NCBI, por sus siglas en inglés) y la Iniciativa Mundial de Intercambio de Datos sobre la Influenza Aviar (GISAID).
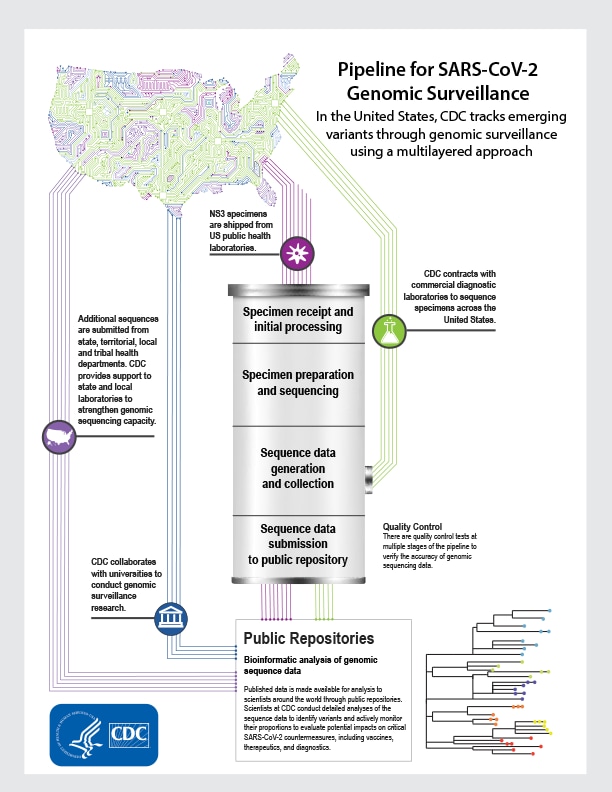
INFOGRAFÍA
Conozca el método de seguimiento de los CDC para las variantes emergentes a través de la red para la vigilancia genómica.
Ver infografía [PDF, 3 MB, 1 página]
Como parte del Sistema de vigilancia de cepas del SARS-CoV-2 (NS3) de los CDC, los laboratorios de salud pública envían muestras anonimizadas a los CDC para generar una muestra representativa de virus para su secuenciación. Hay cuatro etapas principales en el proceso para generar los datos de la secuencia genética del SARS-CoV-2 a partir de estas muestras y ponerlos a disposición en los repositorios públicos.
¿Por qué la vigilancia genómica es importante para la salud pública?
Es importante contar con un sistema integral de vigilancia genética del SARS-CoV-2
- Las mutaciones (sustituciones de nucleótidos) se producen en los virus y se acumulan mediante la constante propagación viral; estas mutaciones generan variantes que pueden tener diferentes atributos. La vigilancia genómica identifica las variantes en circulación para contar rápidamente con la información necesaria para implementar los esfuerzos de respuesta de salud pública.
- Los programas de vacunación, tratamientos y realización de pruebas pueden mejorarse con base en una vigilancia actualizada periódicamente de las variantes, incluida la actualización de las futuras vacunas, si fuese necesario.
- La detección de variantes que son más transmisibles o que causan una enfermedad más grave, nos permite estar preparados en caso de un brote, nos aporta información para las medidas de prevención y fortalece la respuesta de salud pública.
Proceso de secuenciación genómica para el SARS-CoV-2*
- Procesamiento inicial y recepción de la muestra: se reciben las muestras y se ingresan al sistema de información del laboratorio.
- Secuenciación y preparación de las muestras: se extrae el ARN del SARS-CoV-2 y se convierte en ADN complementario, se mejora y se ingresa al equipo de secuenciación de última generación.
- Recolección y generación de datos de secuencias: las muestras son secuenciadas, se recopilan los datos de los secuenciadores y se toman las primeras medidas de control de calidad. Se procesan los datos en crudo y se convierten en datos secuenciales. En esta instancia, se inicia un proceso paralelo en el que los datos de secuencias recopilados en los laboratorios comerciales se integran a las bases de datos de los CDC para su procesamiento.
- Envío de datos de secuencias a los repositorios públicos: los científicos implementan medidas de control de calidad. Las secuencias que no son recibidas desde un principio por los repositorios públicos se analizan y se vuelve a realizar la secuenciación para ser enviadas nuevamente. Los datos publicados se ponen a disposición de los científicos de todo el mundo a través de los repositorios públicos.
Análisis bioinformático de los datos de secuencia genómica
Los datos publicados se ponen a disposición de los científicos de todo el mundo a través de los repositorios públicos. Habitualmente, los CDC recopilan datos de secuencias genómicas de múltiples fuentes para respaldar la vigilancia nacional. Los laboratorios comerciales les transfieren los datos de las secuencias genómicas a los CDC en el paso 3, cuando son procesados y enviados para su publicación. Los laboratorios de investigación y salud pública y las universidades envían los datos directamente a los repositorios públicos. Los científicos de los CDC realizan análisis detallados de los datos de secuencias para identificar las variantes y monitorean activamente los porcentajes para evaluar los posibles impactos en las contramedidas críticas contra el SARS-CoV-2, incluidas las vacunas, las medidas terapéuticas y el diagnóstico.
Los CDC alientan a los laboratorios de salud pública estatales a "etiquetar" las secuencias generadas y publicarlas en las bases de datos públicos para incluir sus aportes en los análisis de los CDC. El uso estandarizado y consistente de información de etiquetado en las secuencias enviadas mejora nuestra capacidad para buscar, analizar y compartir los datos generados en toda la extensión de los Estados Unidos.
* En varias etapas del proceso se realizan pruebas de control de calidad para verificar la exactitud de los datos de secuenciación genómica.
Dirección del sistema nacional de vigilancia de cepas del SARS-CoV-2 (NS3)
El programa NS3 recopila, analiza y comparte información acerca de la diversidad genética del SARS-CoV-2, el virus que causa el COVID-19. El programa ofrece un sistema integral de vigilancia de la población para que se pueda hacer un seguimiento de la evolución del virus a lo largo del tiempo e identificar las variantes emergentes que puedan incidir en el desempeño de los diagnósticos, las opciones terapéuticas o las vacunas, o en la transmisibilidad del SARS-CoV-2 o la gravedad del COVID-19 en los Estados Unidos. Un punto fuerte digno de mención del NS3 es la recolección habitual de muestras en toda la extensión de los Estados Unidos para apoyar los esfuerzos de caracterización de variantes, lo que brinda datos importantes para tomar decisiones informadas en materia de salud pública.
Gracias a las asociaciones con las agencias de salud pública estatales y locales, los CDC solicitan hasta un total de 750 muestras por semana a todos los estados y jurisdicciones para la secuenciación y posterior caracterización de virus representativos. El programa NS3 tiene tres objetivos principales:
- Monitoreo de virus a nivel nacional: los laboratorios de salud pública de los EE. UU. les envían semanalmente o cada quince días muestras clínicas positivas representativas del SARS-CoV-2 a los CDC para apoyar los esfuerzos federales de secuenciación, análisis genético y caracterización fenotípica de los virus que circulan en nuestra población a lo largo del tiempo. Estos dato también se suman al repositorio de datos públicos de secuencias y muestras del SARS-CoV-2.
- Vigilancia mejorada: desde la aparición del SARS-CoV-2, los esfuerzos de secuenciación a nivel nacional y mundial han identificado cambios en el genoma del SARS-CoV-2 como resultado de la transmisión y evolución en seres humanos y animales. Estos cambios genéticos pueden incidir en muchos aspectos de la salud pública, como la transmisión, la gravedad de la enfermedad, el diagnóstico, las opciones terapéuticas y las vacunas. Como parte de la vigilancia mejorada del NS3, los CDC pueden solicitar muestras adicionales a los laboratorios de salud pública para investigar variantes de interés, variantes de preocupación u otras clasificaciones virales específicas, o casos de infección en vacunados.
- Caracterización del virus: según los análisis genómicos, las variantes del SARS-CoV-2 se aíslan de las muestras positivas proporcionadas por los laboratorios de salud pública de los EE. UU. Estos virus aislados son analizados en los laboratorios de los CDC para conocer su posible impacto en las vacunas, tratamientos y diagnósticos actuales, así como su riesgo para la salud pública en general.
A medida que los laboratorios aumentaron su capacidad de secuenciación, los CDC se esfuerzan por mejorar y crear una infraestructura técnica y procesos de trabajo adicionales que garanticen el envío eficiente de los datos de secuencias a los repositorios públicos, que almacenan datos de secuencias de acceso público para que los científicos los incluyan en sus análisis. La secuenciación de última generación es un proceso de varias etapas que involucra procesos de trabajo tanto de laboratorios como de herramientas bioinformáticas. El período que transcurre a partir de que los CDC reciben la muestra hasta que está lista la secuencia para su envío a las bases de datos públicas es de aproximadamente 10 días. Por lo general los plazos son similares para los socios estatales, locales, académicos y comerciales.
Los datos de secuencia genética generados por los CDC y los laboratorios de salud pública locales y estatales son enviados a bases de datos de acceso público gestionadas por el Centro Nacional de Información Biotecnológica (NCBI, por sus siglas en inglés) y la Iniciativa Mundial de Intercambio de Datos sobre la Influenza Aviar (GISAID). La integración de la vigilancia en todo los Estados Unidos aprovecha al máximo la capacidad de secuenciación, la experiencia y los datos disponibles para tomar decisiones informadas en materia de salud pública.
Asociación con laboratorios de diagnóstico comerciales
Además del programa NS3, los CDC firmaron convenios con importantes laboratorios comerciales de diagnóstico para realizar la secuenciación de muestras en toda la extensión de los Estados Unidos. Estos convenios garantizan el acceso constante a los datos de secuencias del SARS-CoV-2 a nivel nacional para complementar los esfuerzos de secuenciación de salud pública existentes.
Colaboración con universidades
Los CDC han financiado a 29 universidades para realizar investigaciones de vigilancia genómica en colaboración con agencias de salud pública. Los estudios permiten profundizar en la genómica viral y la epidemiología molecular dentro de las diferentes regiones del país. Esta información incluye:
- Investigación sobre brotes y vigilancia genómica
- Infección en vacunados
- Resultados de los pacientes y factores de riesgo de enfermarse gravemente
- Transmisión en escuelas e institutos de educación superior o en sus alrededores
Estas colaboraciones generan y potencian las capacidades de secuenciación y bioinformática de todo el país, que son componentes necesarios de una infraestructura integral de salud pública.
Apoyo a los departamentos de salud estatales, territoriales, locales y tribales
Desde el 2014, el programa de detección molecular avanzada de los CDC ha estado incorporando la secuenciación de última generación y las capacidades bioinformáticas al sistema de salud pública de los EE. UU. Muchos departamentos de salud locales y estatales usan la secuenciación genómica como parte de su respuesta ante la pandemia de COVID-19. La secuenciación realizada por los departamentos de salud pública puede ayudar a comprender mejor la epidemiología y la transmisión a nivel local, y estos datos pueden ayudar a investigar los conglomerados de casos en diversos entornos, como los establecimientos de atención médica. Los departamentos de salud pública estatales y federales apoyan las investigaciones locales, llevan a cabo estudios y ponen los datos genómicos a disposición de las bases de datos públicas. Para apoyar aún más estos esfuerzos, se destinaron más de $250 millones a los departamentos de salud pública desde el inicio de la pandemia de COVID-19.
Dirección del consorcio de secuenciación del SARS-CoV-2 para la respuesta a la emergencia de salud pública, epidemiología y vigilancia (SPHERES)
Desde el inicio de la pandemia de COVID-19, los CDC han encabezado un consorcio nacional de laboratorios de secuenciación del SARS-CoV-2, conocido como SPHERES. El consorcio SPHERES está conformado por más de 250 instituciones, que incluyen a aproximadamente 1 200 científicos en los Estados Unidos, como centros académicos, la industria, organizaciones no gubernamentales y agencias de salud pública.
Estos esfuerzos permiten:
- Coordinar el análisis de datos y la secuenciación en todo el país
- Alentar la colaboración y el uso de estándares de datos, protocolos y mejores prácticas
- Garantizar que los datos genómicos generados sean de la más alta calidad y generen el mayor impacto para la salud pública y la comunidad de investigación en general
Caracterización de virus
Los CDC analizan los datos genómicos disponibles y brindan actualizaciones semanales:
- Secuencias del SARS-CoV-2 publicadas
- Proporciones de las variantes del SARS-CoV-2
- Proporciones de variantes del SARS-CoV-2 con sustituciones de preocupación terapéutica.
Estos análisis dan lugar a la selección y priorización de un subgrupo de virus representativos para su posterior caracterización. Los esfuerzos de caracterización del virus pueden incluir la evaluación de la capacidad de los anticuerpos generados luego de una infección o vacunación previa para neutralizar los virus en circulación, la susceptibilidad de los virus a los tratamientos autorizados y los estudios de laboratorio para evaluar la transmisibilidad del virus y la patogénesis. Los datos de virus aislados se comparten con socios de salud pública, académicos, agencias federales y socios comerciales a través de Recursos de BEI.
Para recibir actualizaciones del COVID-19, ingrese su dirección de correo electrónico: